|
今日,最新一期《自然》杂志如约上线,而登上封面的“癌症全基因组”则是本期的主题:在本期《自然》杂志上,一共发表了6篇相关的论文。而在Nature Genetics、Nature Biotechnology、以及Nature Communications等子刊上,也有系列论文发表。
那么,是什么样的研究项目引起了如此的重视呢?具体来看,主导这些研究的是“泛癌症全基因组分析合作项目”(Pan-Cancer Analysis of Whole Genomes Consortium),而“全基因组”是其中的关键词。过去,很多研究都在寻找哪些编码蛋白质的基因在突变后会导致癌症。但事实上,编码蛋白质的基因序列,仅为人类基因组的约2%。在剩下的98%中有哪些变异可能与癌症有关,我们尚不是非常了解。而这正是“全基因组分析”的意义所在。
在这个合作项目的主导下,来自全球四个大洲744个组织的科研人员们对2658份癌症样本做了全基因组测序工作,涵盖了38种不同的癌症类型。此外,来自同一名个体的非癌变样本也被用于对照。从获取样本、保护患者隐私、获取测序数据、分析测序数据等一系列流程来看,这一研究的工作量极为庞大。而这些努力,也最终带来了可喜的回报。对于癌症全基因组,我们有了新的认识。

平均来看,每一个肿瘤基因组样本里,大约有4到5个驱动癌症发展的突变,这会给这些癌细胞带来生存上的选择性优势。《自然》的一篇总结性文章里也提到,研究中使用的肿瘤样本里,很多出现了复杂的DNA重排(17.8%为chromoplexy,22.3%为chromothripsis,这两个单词的解释请见下图)。相比之下,只有5%的样本没有查出驱动性的突变。
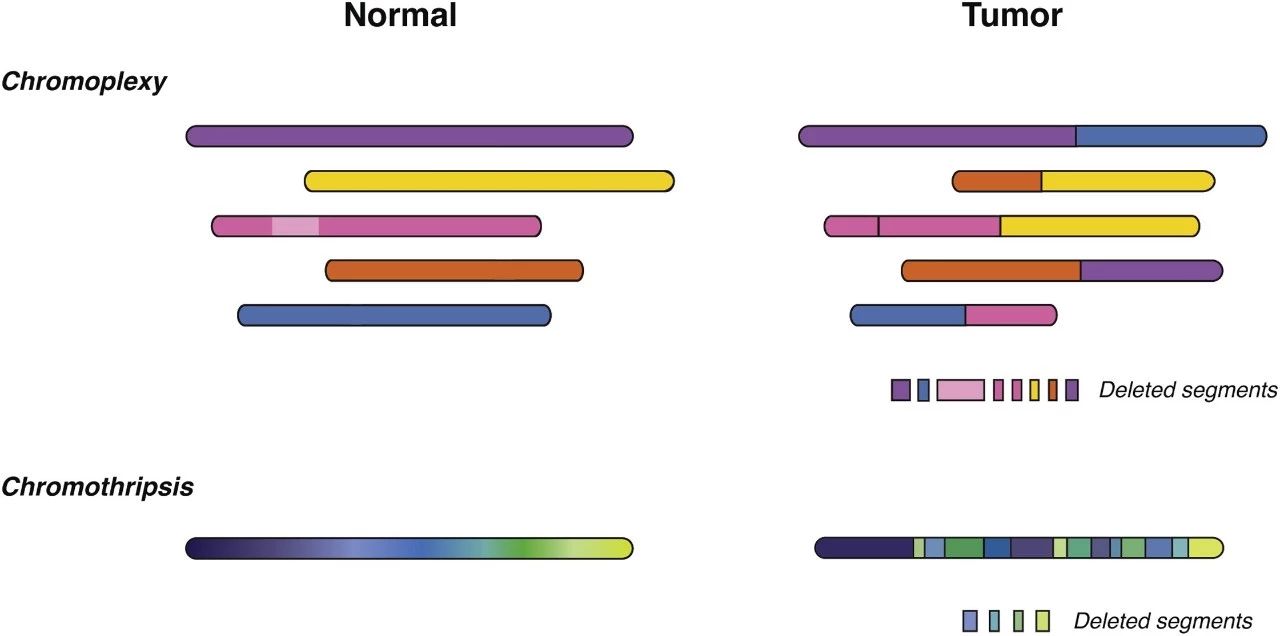
▲Chromoplexy与chromothripsis的形象化解释(图片来源:参考资料[8])

第二篇文章里,研究人员们则尝试从非编码DNA里寻找癌症的驱动因素。研究发现了一些全新的癌症驱动突变,譬如抑癌基因TP53的一段非编码区里,反复出现了一种突变;而编码端粒酶的基因TERT的非编码区,也有会导致其过度表达的突变。这或许会促进癌细胞异常分裂。

第三和第四篇文章侧重讲的是一些具有特征性的基因组变异。这是啥意思呢?原来当DNA修复出现错误,或是接触到环境里的诱变剂时,都会在DNA里留下一些具有特征性的变化,但这些变化并不好找。研究人员们在大量数据的支持下,找到了97个类似的特征性变化,极大地拓展了我们的认知。
|